
在调查犯罪时,法医专家有时会使用DNA证据来识别犯罪嫌疑人。然而,DNA不仅包含识别信息,还有我们基因构成的线索。DNA 分离可以用来深入研究 DNA 链,但是传统方法很耗时。为了加快 DNA 的分离,密苏里科技大学的研究人员使用了 COMSOL Multiphysics® 软件。
我们的基因构成
DNA 的分子结构很复杂:它是由长链核苷酸组成的双螺旋聚合物。通过将样本分解成大小不同的片段,可以使研究 DNA 变得更加容易。
DNA 核苷酸或碱基对是鸟嘌呤(G),腺嘌呤(A),胸腺嘧啶(T)和胞嘧啶(C)。研究人员试图在基因组测序和医学诊断等领域中理解这些遗传“字母”的序列,例如,以定位基因并了解它们如何在生物体内协同工作。如果没有 DNA 分离,这项工作就不容易做到,毕竟,人类基因组拥有超过 30 亿个碱基对 DNA!
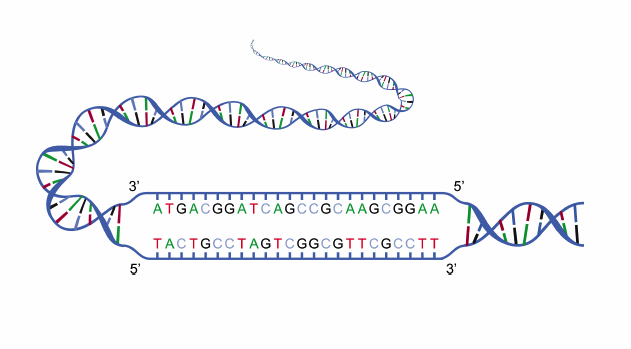
图示为包含有碱基对字母 G,A,T 和 C 的 DNA 链。图像来源于美国公共领域 Wikimedia Commons 。
最近,其他一些 DNA 分析的例子也成为了人们关注的焦点。您可能熟悉邮寄 DNA 测试工具包,它可帮助您了解有关您祖先的更多信息。当基因检测公司将您的DNA样本数字化时,它看起来像核苷酸 G,A,T 和 C 字母的长链。这些公司使用算法将您的基因组的 DNA 片段与参考数据集进行比较。然后,算法确定您的DNA样本与每个参考集的匹配程度,以查看您最可能属于哪个血统。该算法的性能取决于它的参考集,因此与数据库中的其他组相比,一些血统的代表性可能不足。
在法医学等领域,DNA 分析有助于科学家比较遗传物质的样本。由于很少有两个人具有相同的DNA模式,因此法医科学家可以将 DNA 分子切片中的模式与参考数据库进行比较,例如美国联邦调查局管理的联合 DNA 索引系统(CODIS)。然而,像 CODIS 这样的系统仅限于它们包含的 DNA 谱。调查人员开始使用上述提到的血统数据库,通过一个名为家族 DNA 的概念扩展他们的搜索范围。例如,在 2018 年,警方调查金州杀人案时,将犯罪现场 DNA 与家谱网站数据库进行了对比,发现了与远房亲属的部分匹配。最终,这有助于他们缩小搜索范围并识别被指控的犯罪嫌疑人。
用 DNA 分离技术研究核苷酸链中的片段链接
凝胶电泳是一种用于分离DNA分子(主要是在法医中)的常用技术,该技术涉及通过凝胶迁移带负电的核酸分子。当施加电流时,较小的分子穿过凝胶的速度比较大的分子快,因此碎片会根据大小分成条带。为了使这种分离可视化,我们使用了放射性染料。
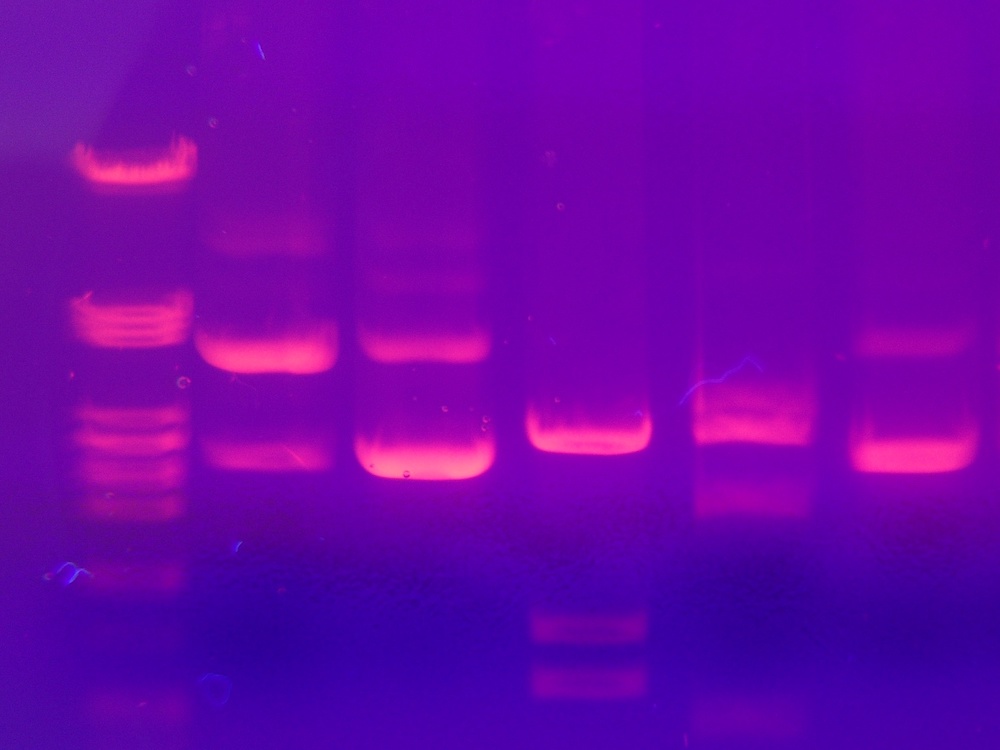
凝胶电泳结果示例。图片来自Mnolf的研究 。在Wikimedia Commons中获得CC BY-SA 3.0许可。
还有另一种方法可以在不使用凝胶或电场的情况下更有效地分离 DNA 长链:熵捕获。在这种基于微芯片的系统中,建立不同高度的熵阱阵列(结构化微通道),以使狭窄通道间隙远小于 DNA 分子的旋转直径。根据链长分离分子,当带负电荷的 DNA 分子通过电泳力驱动通过这些通道时,洗脱时间取决于 DNA 分子的长度。DNA 分子越长,它被吸入狭小通道的可能性越大,因为较长的分子占据更多的表面积。

熵陷阱的示意图,宽通道中的 DNA 分子将流入窄通道。图片由密苏里科技大学提供。
尽管熵捕获比其他分离方法更快且更有效,但所需设备的设计和制造需要花费大量的时间并且成本高昂,因为它依赖于反复试验。自从发现熵捕获方法以来,研究人员已经进行了计算研究以优化设计并研究这些设备中的分离机制,但是至今尚未使用商业软件来模拟这些熵诱捕系统。
使用COMSOL Multiphysics®来模拟熵陷阱系统中的聚合物动力学
为了确定它们是否可以通过商用模拟软件以节省时间,密苏里科技大学的研究人员使用COMSOL Multiphysics®建立了熵陷阱系统和聚合物动力学模拟,并将其结果与实验数据进行了比较。
由Joontaek Park,James Jones,Meyyamai Palaniappan,Saman Monjezi和Behrouz Behdani组成的研究小组表示,“微通道模拟中的DNA动力学具有挑战性,因为必须进行两种不同的模拟:复杂的微流体几何以及聚合物分子动力学中的场计算—-他们补充道“幸运的是,COMSOL®可以相对轻松地处理这些模拟,并且COMSOL®在DNA或单聚合物分子模拟区域打开了新的一页。”
该团队使用附加的粒子追踪模块对DNA链进行了布朗动力学模拟。借助CFD模块,在牛顿流体中将链设置为单聚合物珠链模型。至于珠子本身,它们被当作布朗粒子处理,以解决链条穿过周围溶剂时链条的随机运动。
为了描述每个珠子之间的弹力,他们使用了另一个众所周知的模型,即蠕虫状链(WLC),该模型描述了半柔性聚合物的行为。除了WLC之外,研究团队还利用Lennard-Jones势来防止珠子相互渗透。在设置熵阵列几何结构(如下所示)以使Hs远小于典型DNA分子的旋转直径后,研究人员使用 AC/DC 模块在整个通道上创建了电势电场。
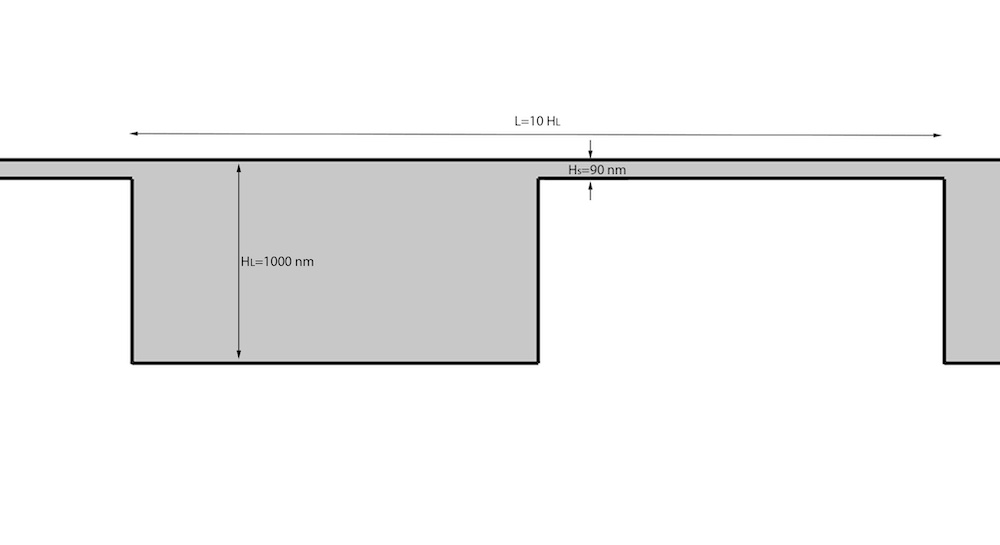
模拟中使用的通道结构示意图。图片由密苏里科技大学提供。
评估模拟结果
研究小组使用有限元法计算了非均匀电场。这里可以看到电场的方向,箭头也指示了DNA分子移动的方向。
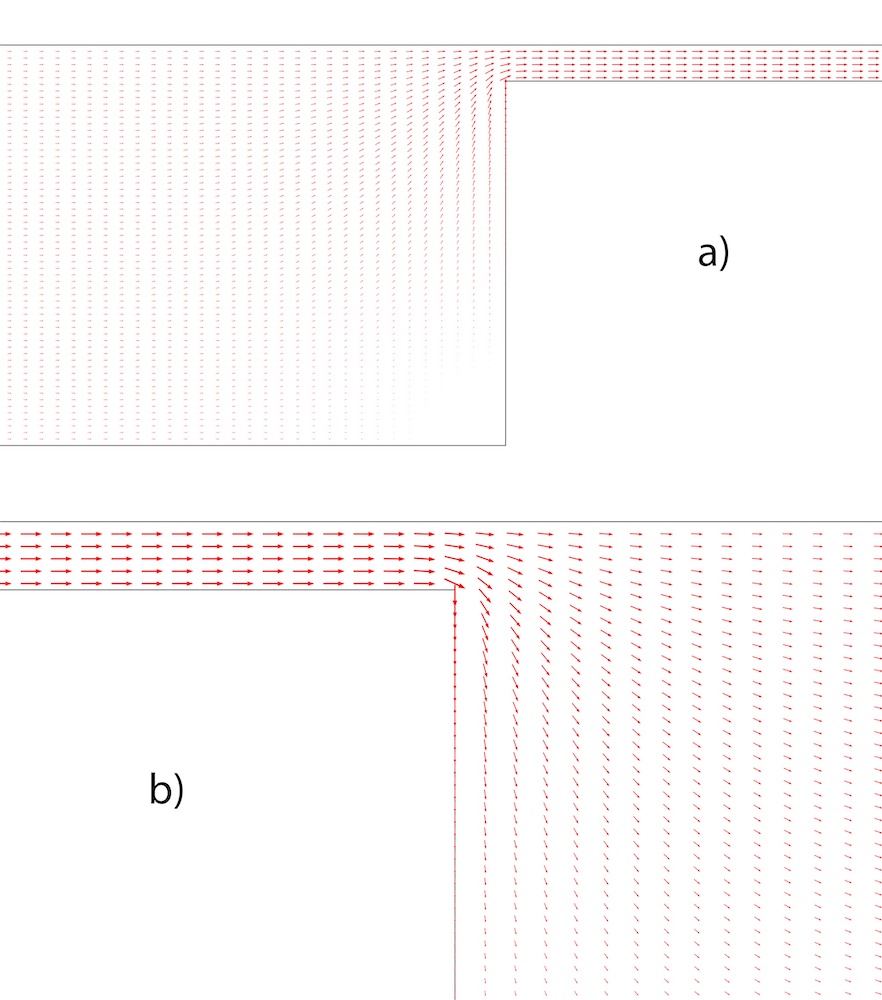
宽通道的右角(a)和左角(b)中的电场通量矢量。图片由密苏里科技大学提供。
接下来,研究人员根据长度,在Nb = 2,4 和 16 个珠子长度下模拟 DNA 分子的质心运动轨迹,因为它们周期性地流入收缩通道。每个分子以相同距离行进的轨迹如下所示。正如上面的电场矢量所预期的那样,分子在狭窄的通道中移动得更快,并且分子越长(它具有的珠子越多),它移动得越快。同时,较短的分子沿其轨迹速度在降低,并且DNA分子的分布表明扩散性更强,通过将它们从电场最强的区域移开而降低了通过通道的总速度。
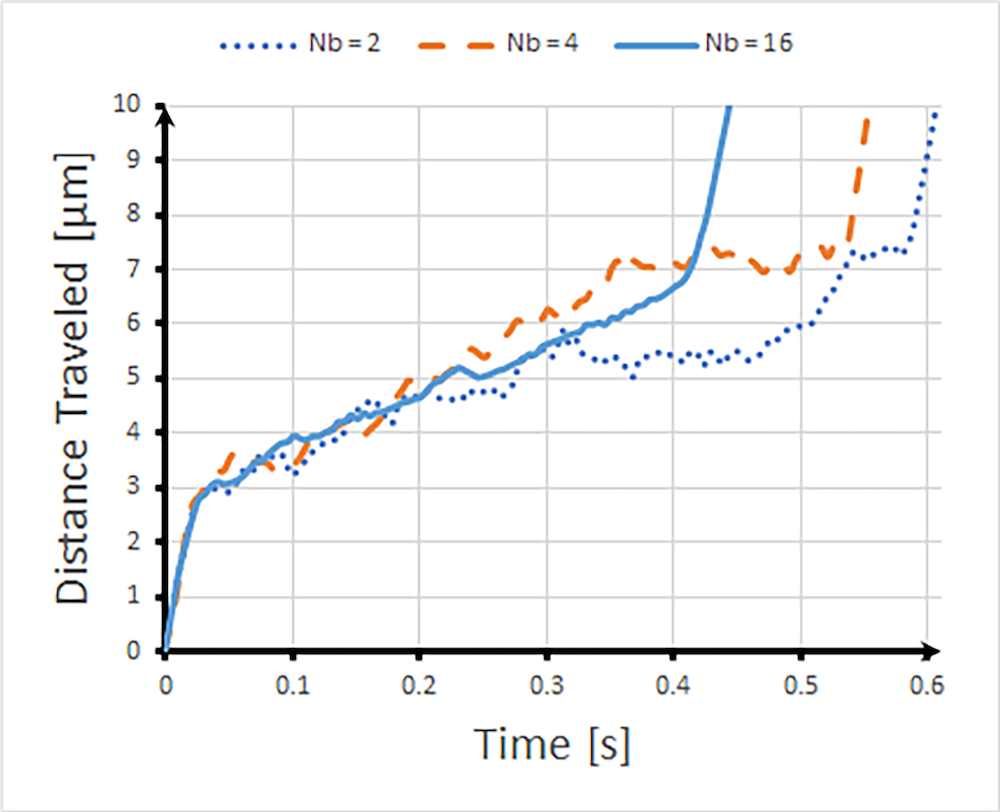
Nb = 2,4 和 16 的 DNA 分子的质心运动轨迹。图片由密苏里科技大学提供。
这种比较可以在下面的动画中看到,短珠长度Nb = 2,中间珠长Nb = 4,长珠长度Nb = 16。如图例中的单位所示,动画中的颜色显示粒子在任何时间点的速度。正如预期的那样,DNA分子的表面越大,它越有可能被拖入更小的通道。(请注意,动画比实时约慢 10 倍。如果您希望进一步减慢速度,可以将鼠标悬停在动画上,然后单击齿轮图标。)
Nb = 2 个较短的 DNA 分子在熵阱通道中的宽通道流入或流出。动画由密苏里科技大学提供
Nb = 4 个中长 DNA 分子在熵阱通道中的宽通道流入或流出。动画由密苏里科技大学提供。
Nb = 16 个较长的分子在熵阱通道中的宽通道流入或流出。动画由密苏里科技大学提供。
研究人员能够证实,他们的模拟结果与熵陷阱中DNA链轨迹的实验数据非常一致,这些结果表明,较长的 DNA 链确实比较短的链能更快地洗脱。
使用 COMSOL Multiphysics 进行聚合物动力学模拟为进一步的研究开辟了可能性,因为这是使用商用软件进行此类模拟的第一次试验。该团队表示“COMSOL Multiphysics 是一种非常受欢迎且用户友好的仿真工具”,此外,使用该软件进行聚合物动力学的扩展将“增强相关的应用和模拟研究”。
至于自己未来的研究呢?该团队补充说,他们可以进行对惯性效应,聚合物构型(支化聚合物)效应以及DNA-碳纳米管相互作用的研究。
下一步
有关密苏里科技大学研究人员工作的更多详细信息,请单击下面的按钮:
参考
- S. Monjezi, B. Behdani, M.B. Palaniappan, J.D. Jones和J. Park,“微加工装置中DNA分离的计算研究:一般方法和最新应用综述”,Adv. in Chem. Eng. Sci.,7 (4), pp. 362–393, 2017。





评论 (2)
沁航 刘
2021-11-22Hello! Can a case MPH file be provided for study?
E-mail: 584221818 @qq.com
Thank you very much!
hao huang
2021-11-24 COMSOL 员工we are so sorry, there is no relevant case available.